Mon Mar 09 2026
三基因 PDAC Panel 综合补充报告
这页不是把原始导出目录原样挂出去,而是把它整理成站内的一篇研究笔记。读者现在可以直接在网页里看摘要、预览图和关键统计表;需要追溯时,再下载对应的 PDF 和 CSV。
这份页面把原来那份单页静态报告拆成了站内可读版本。核心结论没有变,但现在图版、统计表、 下载入口和摘要说明都直接纳入现有网站结构,不再依赖原始导出目录。
Cohort
345
TCGA/GTEx expression comparison · 178 tumor + 167 normal
Cohort
178
TCGA-PAAD survival analysis · 178 matched patients
Cohort
130
GSE62452 control vs disease · 61 control + 69 disease
Cohort
69
GSE62452 early vs late stage · 50 early + 19 late
Tumor-normal 主信号
CDH1 +0.360
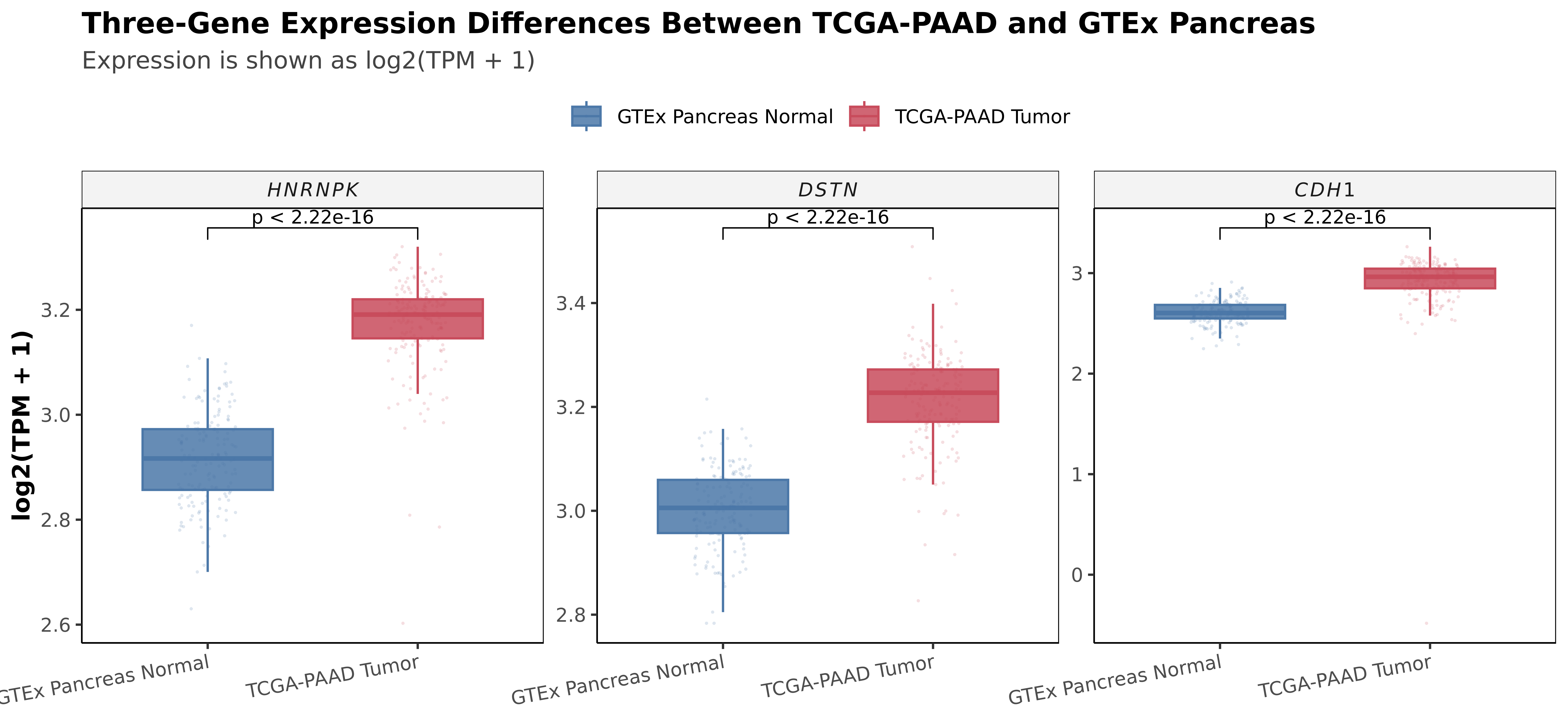
TCGA / GTEx 比较中,三基因都上调,幅度最大的是 CDH1。
Disease 判别
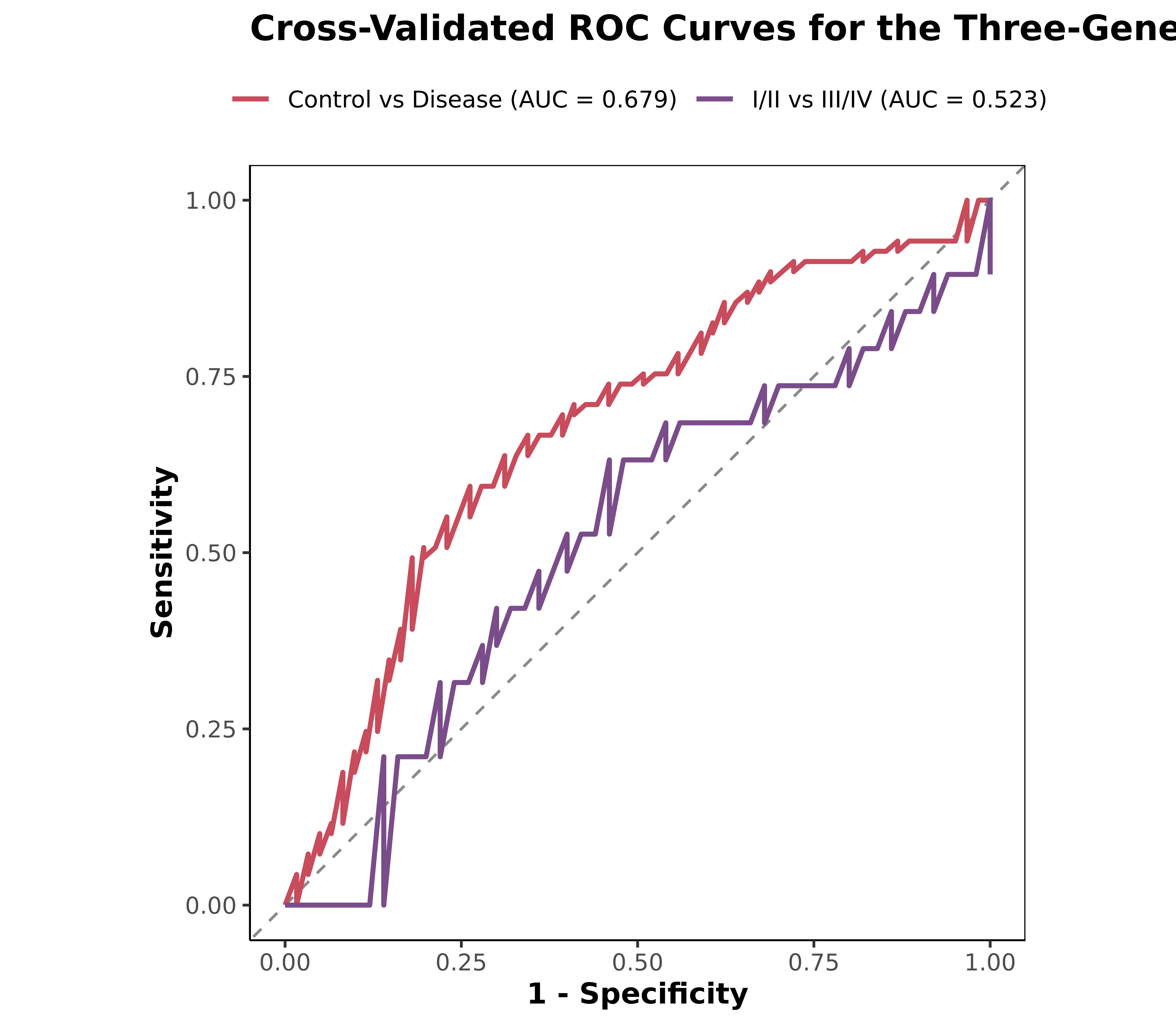
AUC 0.679
Control vs Disease 的 balanced accuracy 为 0.634,明显强于分期任务。
Stage 判别
AUC 0.523
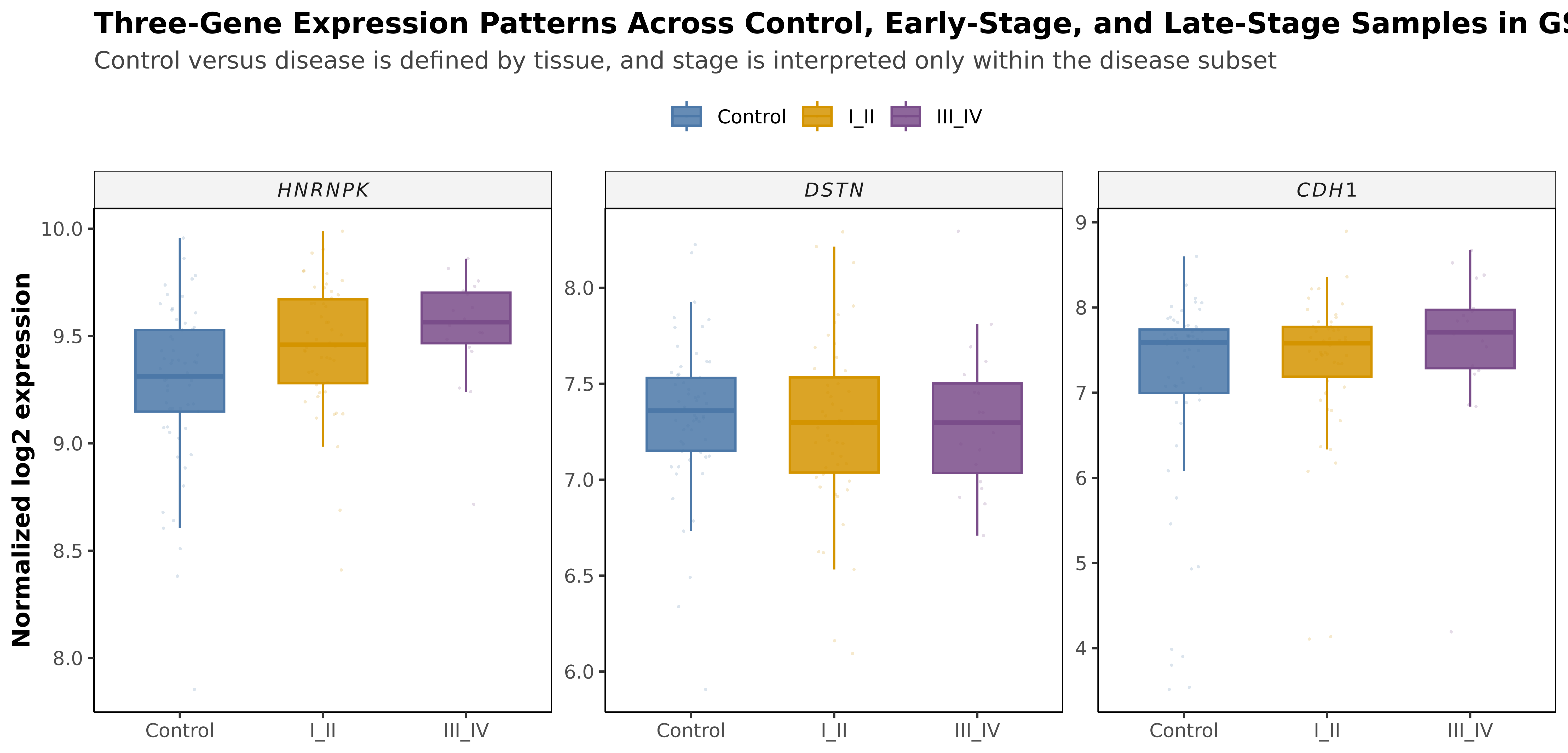
Early vs Late 的 sensitivity 为 0.000,说明这组三基因并不适合单独承担分期识别。
预后证据
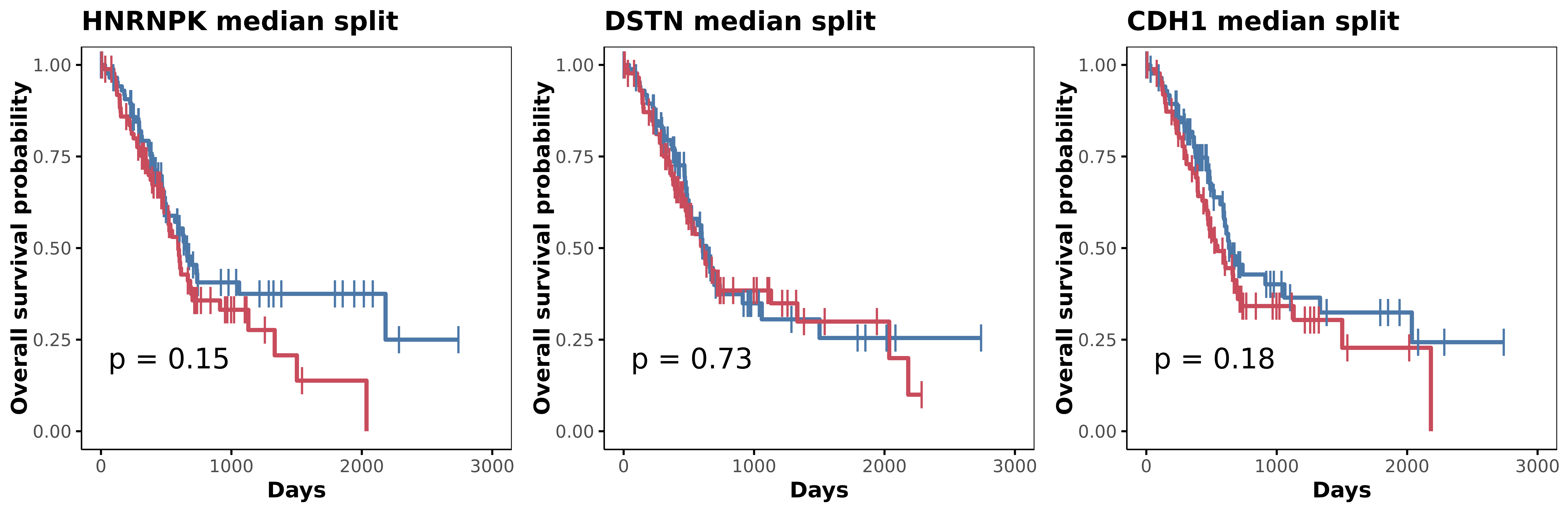
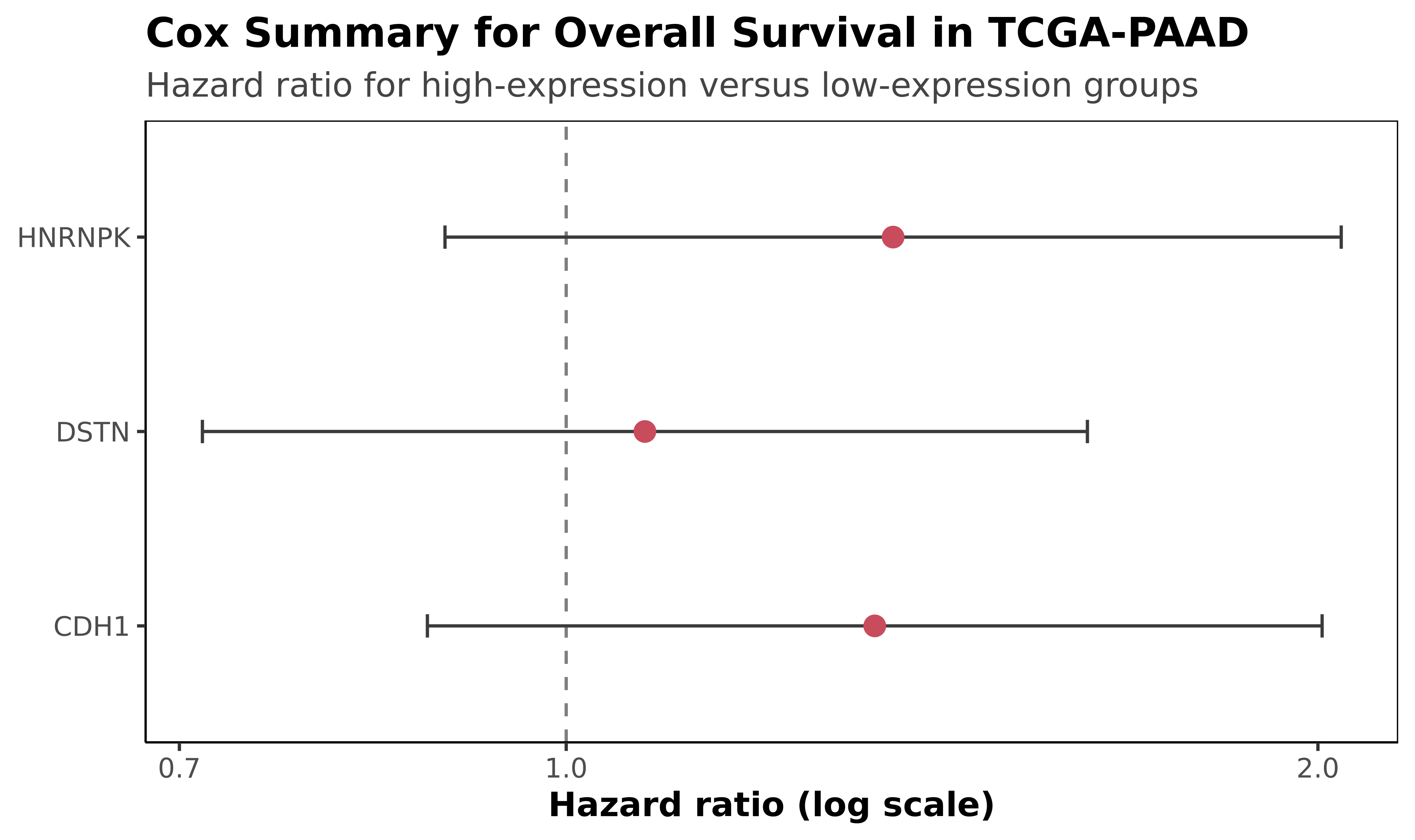
HR 1.352
最高 HR 来自 HNRNPK,但所有单基因 Cox FDR 都未达显著。
结论 1
HNRNPK、DSTN、CDH1在 TCGA-PAAD 相对正常胰腺中整体上调,说明 panel 确实贴着 disease-state 主轴。
结论 2
GEO 独立验证里,只有 HNRNPK在 control vs disease 上给出了相对稳定的外部队列信号。
结论 3
当前证据更支持它是 疾病检测相关 panel,而不是已经成熟的预后 panel。
图版总览
预览图来自原报告内嵌渲染结果,PDF 则作为正式图件保留,阅读和下载都直接走站内路径。
6 figures
关键统计表
页面只展开高信息密度的几张表,其余 CSV 都保留下载入口。这样既能在网页里读,又不会退回到 “挂静态目录”的做法。
TCGA / GTEx 表达差异
3 genes · median shift / p / FDR
TCGA / GTEx 表达差异
3 genes · median shift / p / FDR
| Gene | Shift | p | FDR |
|---|---|---|---|
| HNRNPK | +0.274 | <0.001 | <0.001 |
| DSTN | +0.222 | <0.001 | <0.001 |
| CDH1 | +0.360 | <0.001 | <0.001 |
TCGA 生存分析
3 genes · HR / Cox p / FDR
TCGA 生存分析
3 genes · HR / Cox p / FDR
| Gene | HR (95% CI) | Cox p | FDR |
|---|---|---|---|
| HNRNPK | 1.352 (0.894-2.043) | 0.153 | 0.265 |
| DSTN | 1.075 (0.715-1.617) | 0.727 | 0.727 |
| CDH1 | 1.329 (0.880-2.008) | 0.176 | 0.265 |
GSE62452 二分类表现
2 models · AUC / accuracy / balance
GSE62452 二分类表现
2 models · AUC / accuracy / balance
| Model | AUC | Accuracy | Balanced accuracy |
|---|---|---|---|
| Control vs Disease | 0.679 | 0.638 | 0.634 |
| Early vs Late Stage | 0.523 | 0.710 | 0.490 |
GEO 内部的 disease / stage 差异
两张表合并展示,便于对比 HNRNPK 的外部稳定性
GEO 内部的 disease / stage 差异
两张表合并展示,便于对比 HNRNPK 的外部稳定性
| Disease | Shift | p | FDR |
|---|---|---|---|
| HNRNPK | +0.202 | <0.001 | 0.001 |
| DSTN | -0.062 | 0.341 | 0.341 |
| CDH1 | +0.027 | 0.175 | 0.262 |
| Stage | Shift | p | FDR |
|---|---|---|---|
| HNRNPK | +0.105 | 0.204 | 0.306 |
| DSTN | -0.001 | 0.941 | 0.941 |
| CDH1 | +0.128 | 0.173 | 0.306 |
综合汇总
HNRNPK 的 GEO disease shift 为 +0.202,是三基因里最稳定的独立队列表现
综合汇总
HNRNPK 的 GEO disease shift 为 +0.202,是三基因里最稳定的独立队列表现
| Gene | TCGA shift | HR | GSE disease | GSE stage |
|---|---|---|---|---|
| HNRNPK | +0.274 | 1.352 | +0.202 | +0.105 |
| DSTN | +0.222 | 1.075 | -0.062 | -0.001 |
| CDH1 | +0.360 | 1.329 | +0.027 | +0.128 |
下载与复现
原始导出目录已经被拆掉;现在站内保留的是整理后的图件、预览和 CSV。后续即使删除 `2026-03-supply_unified/`,这个页面和这些附件也能继续独立存在。
队列概览
四个分析任务的样本量与分组结构。
table_01_overview.csv
TCGA / GTEx 表达统计
三基因的 tumor-normal 中位数差、p 值与 FDR。
table_02_tcga_gtex_expression_stats.csv
TCGA 生存统计
单变量 Cox 与 log-rank 结果。
table_03_tcga_survival_stats.csv
GSE disease 统计
独立 GEO 队列中 Control vs Disease 的基因差异。
table_04_gse_disease_stats.csv
GSE stage 统计
肿瘤早晚期内的表达差异。
table_05_gse_stage_stats.csv
二分类指标
AUC、准确率、敏感性、特异性与平衡准确率。
table_06_gse_binary_metrics.csv
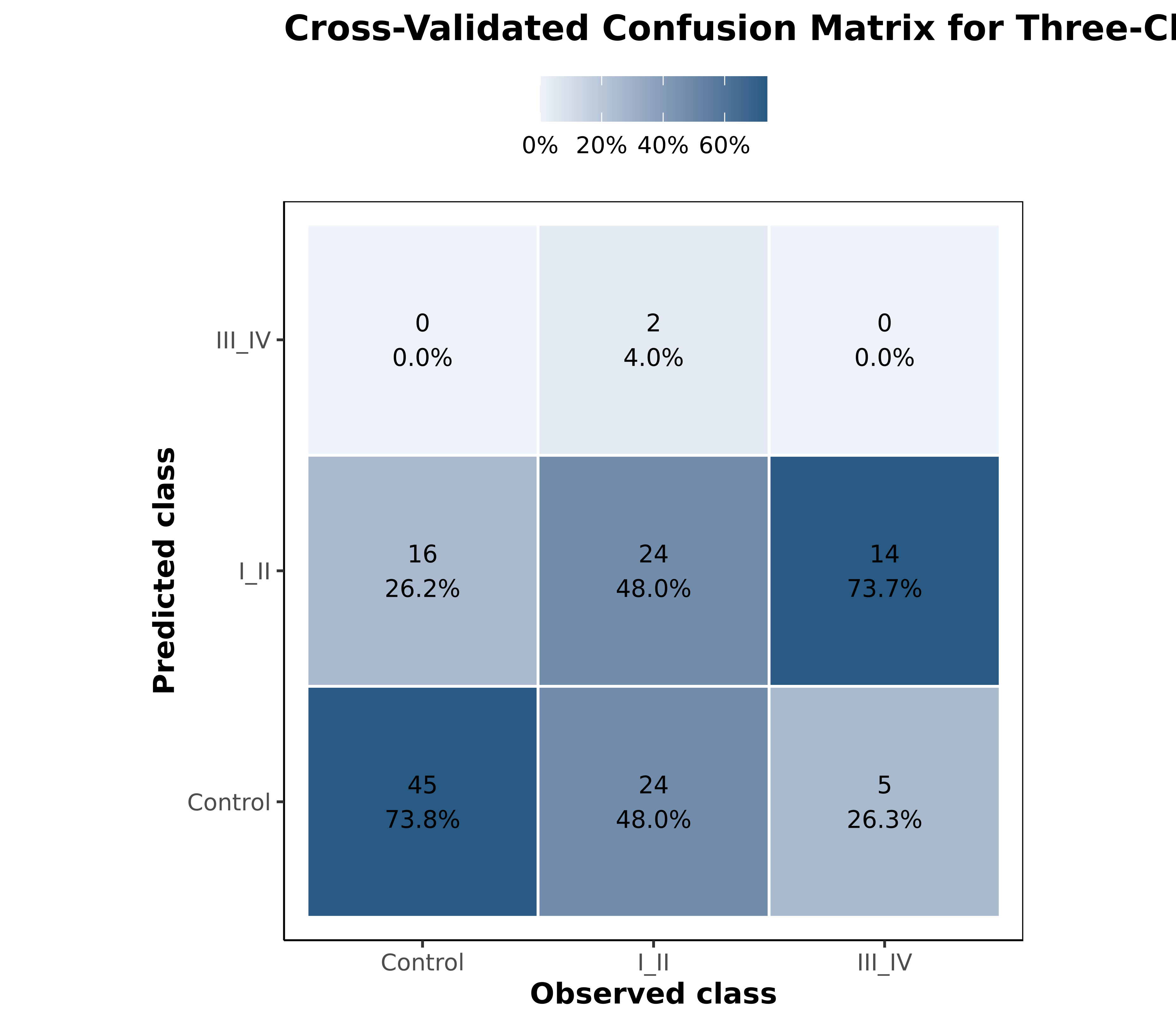
三分类指标
三分类任务的 accuracy 与 kappa。
table_07_gse_multiclass_metrics.csv
综合汇总
表达差异、生存信号与 GEO 表现的整合视图。
table_08_integrated_summary.csv